HS Taq DNA Polymerase, 500U
R$178,35
HS Taq DNA Polymerase
P1082 (500U)
Concentração: 5 U/ul
Conteúdo
HSTM Taq DNA Polymerase – 100ul
10 x HSTM PCR Buffer (Mg2+ Plus) – 1.25ml
6x Loading Dye – 1ml
Descrição
HSTM Taq DNA Polymerase é uma enzima DNA polimerase termoestável derivada da bactéria Thermus aquaticus. O peso molecular da enzima é de 94kDa. HSTM Taq DNA Polymerase pode amplificar DNA de até 5kb. A velocidade de amplificação é de 0.9~1.2kb/min. A enzima tem atividade exonuclease 5’ – 3’, mas, não tem atividade 3’ – 5’ o que resulta em finalização com 3’-dA no produto da PCR.
Todos os componentes do HSTM PCR Buffer tem uma concentração ótima para amplificação eficiente. A atividade termoestável contribui para incorporação específica dos primers na amostra.
10 x HSTM PCR Buffer (Mg2+ Plus)
200mM Tris-Cl (pH 8.8), 100mM KCl, 16mM MgSO4 1% Triton-X-100
Aplicações
- PCR – amplificação de fragmentos de DNA de até 5kb
- Conjugação de DNA
- Sequenciamento de DNA
- PCR para clonagem
Armazenar a -20°C
Apenas para uso em pesquisa
Disponível por encomenda
Produtos relacionados
-
R$1.863,40Adicionar ao carrinho
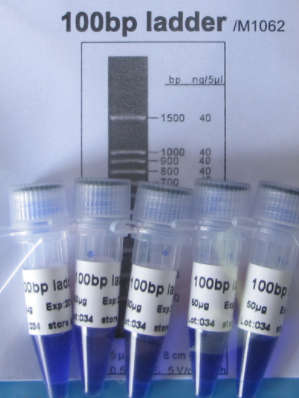
100bp DNA ladderM1062 (5 x 50ug)
Concentração: 100ng/ul
Armazenar a -20°C
Volume estimado: 5x500ul
Descrição
100bp DNA ladder é ideal para determinar o tamanho de DNA de fita dupla de 100 a 1.500 pares de base. O marcador consiste em 11 fragmentos lineares de dupla fita. O fragmento de tamanho 500bp está presente com maior intensidade para permitir fácil identificação. Todos os fragmentos são precisamente quantificados e misturados durante a fabricação. Para aplicação de 5ul, todos os fragmentos têm 40ng, com exceção do fragmento 500bp que tem 100ng. Este marcador é pré-misturado com tampão de aplicação azul e está pronto para uso.
Aplicação recomendada
2-5 ul por poço
Concentração
Banda em evidência 100 ng/5ul
Outras bandas 40 ng/5ul
Condições recomendadas para Eletroforese
Gel de agarose 1.7%, 8 cm, 0.5X TAE, 5 V/cm, 1h.
Conteúdo (bp)
100, 200, 300, 400, 500, 600, 700, 800, 900, 1.000 e 1.500 -
R$346,06Adicionar ao carrinho
Descrição
A digestão de Hind III de DNA lambda produz 8 fragmentos adequados para uso como
padrões de peso molecular para eletroforese em gel de agarose. DNA / Hind Ⅲ é pré-misturado com tampão de carregamento e está pronto para uso.Condição de eletroforese recomendada
8 cm, gel de agarose 0,7%, 1 × TAE, 7 V / cm, 45 min.Conteúdos (bp)
125, 564, 2.027, 2,322, 4,361, 6,557, 9,416, 23,130.Armazenar
Estável por 3 meses em temperatura ambiente, para armazenamento a longo prazo, armazene a -20 ℃.Atenção!
As extremidades coesivas dos fragmentos 1 e 4 podem causar a formação de banda extra de 27491 bp. Os fragmentos podem ser separados por aquecimento a 65 ° C por 3 minutos antes de carregar a amostra no gel.
-
R$122,45Adicionar ao carrinho
Gel Loading Dye (6X)
M9041 (5 x 1ML)Armazenar em temperatura ambiente
Descrição
Gel Loading Dye é um tampão de aplicação 6X concentrado com dois corantes de rastreamento para géis de agarose e de poliacrilamida não denaturante. Incluir EDTA em quelato de magnésio (até 10mM) em reações enzimáticas para parar a reação. Azul de bromofenol e xileno cianol são os corantes padrões para eletroforese.
Conteúdo
10mM Tris-HCl, pH 7.6, 0.03% azul de bromofenol, 0.03% xileno cianol, 60% glicerol, 60mM EDTA
Aplicações
Preparar marcadores de DNA e amostras para aplicação no gel de agarose e poliacrilamida.
Características
Dois corantes para rastreamento da migração do DNA durante a eletroforese.
Sem interferência no DNA durante a exposição à luz UV
EDTA se liga a íons de metais bivalentes e inibe nucleases dependentes de metais.
Ensaio de Controle de Qualidade
Gel Loading Dye (6X) é testado para contaminantes de endonucleases, exonucleases e atividade de RNAse. -
R$798,60Adicionar ao carrinho
Solução RNase A
Grau BR, somente para uso em pesquisa.
Nº N9042 Concentração: 100 mg/ml Tamanho: 1 ml
Atividade Específica: ≥3000 U/mg de proteína (≥60 unidades Kunitz/mg de proteína).
Componentes
Componente N9041 ( 10mg/ml) N9042 (1 00mg/ml) Solução RNase A 1 ml 1 ml Descrição
A RNase A é uma endorribonuclease que degrada especificamente o RNA de fita simples nos resíduos C e U. Ele cliva a ligação fosfodiéster entre a ribose 5′ de um nucleotídeo e o grupo fosfato ligado à ribose 3′ de um nucleotídeo pirimidina adjacente. O fosfato 2′,3′-cíclico resultante é hidrolisado no fosfato 3′-nucleosídeo correspondente.Formulários
-Preparação de plasmídeo e DNA genômico
-Remoção de RNA de preparações de proteínas recombinantes.
–Ensaios de proteção de ribonuclease
–Mapeamento de mutações de base única em DNA ou RNAArmazenar _
-20ºC recomendado.
Monômero de peso molecular
13,7 kDa.