HS Taq DNA Polymerase, 500U
R$178,35
HS Taq DNA Polymerase
P1082 (500U)
Concentração: 5 U/ul
Conteúdo
HSTM Taq DNA Polymerase – 100ul
10 x HSTM PCR Buffer (Mg2+ Plus) – 1.25ml
6x Loading Dye – 1ml
Descrição
HSTM Taq DNA Polymerase é uma enzima DNA polimerase termoestável derivada da bactéria Thermus aquaticus. O peso molecular da enzima é de 94kDa. HSTM Taq DNA Polymerase pode amplificar DNA de até 5kb. A velocidade de amplificação é de 0.9~1.2kb/min. A enzima tem atividade exonuclease 5’ – 3’, mas, não tem atividade 3’ – 5’ o que resulta em finalização com 3’-dA no produto da PCR.
Todos os componentes do HSTM PCR Buffer tem uma concentração ótima para amplificação eficiente. A atividade termoestável contribui para incorporação específica dos primers na amostra.
10 x HSTM PCR Buffer (Mg2+ Plus)
200mM Tris-Cl (pH 8.8), 100mM KCl, 16mM MgSO4 1% Triton-X-100
Aplicações
- PCR – amplificação de fragmentos de DNA de até 5kb
- Conjugação de DNA
- Sequenciamento de DNA
- PCR para clonagem
Armazenar a -20°C
Apenas para uso em pesquisa
Disponível por encomenda
Produtos relacionados
-
R$266,20Adicionar ao carrinho
Descrição
Proteinase K pronta pra usar é uma protease endolítica que cliva ligações peptídicas nos lados carboxílicos de aminoácidos alifáticos, aromáticos ou hidrofóbicos.
A Proteinase K é classificada como uma serina protease. O menor peptídeo a ser hidrolisado por essa enzima é um tetrapeptídeo.Aplicações
- Isolamento de DNA genômico de células e tecidos cultivados;
- Remoção de DNases e RNases ao isolar DNA e RNA de tecidos celulares;
- Melhorar a eficiência de clonagem de produtos de PCR.
Concentração
20 mg /mlBuffer de Armazenamento
A enzima é fornecida em: Tris-HCl 50 mM (pH 7,5), contendo cloreto de cálcio 5 mM e glicerol a 50% (v/v).Inibição e Inativação
Inibidores: a proteinase K não é inativada por quelantes de metal, por reagentes reativos com tiol ou por inibidores específicos de tripsina e quimiotripsina. O fluoreto de fenilmetilsulfonil e o diisopropil fosforofluoridato inibem completamente a enzima.
Inativado por aquecimento a 95 °C por 10 minutos.Observação
- Atividade ótima em 50-55 ° C.
- A desnaturação rápida da enzima ocorre em temperaturas acima de 65 ° C.
- A concentração de trabalho recomendada para Proteinase K é de 0,05-1 mg /ml. A atividade da enzima é estimulada por SDS 0,2-1% ou por uréia 1-4 M.
- O Ca2 + protege a Proteinase K contra a autólise, aumenta a estabilidade térmica e tem uma função reguladora para o local de ligação do substrato da Proteinase K.
- Estável em uma ampla faixa de pH: 4,0-12,5, pH ideal 7,5-8,0
-
R$1.863,40Adicionar ao carrinho
Descrição
O marcador 50 pb é ideal para determinar o tamanho do DNA de fita dupla de 50 a 500 pares de bases. A escada consiste em 8 fragmentos lineares de fita dupla. O fragmento de 250 pb está presente em intensidade aumentada para permitir fácil identificação. Todos os fragmentos são quantificados com precisão e misturados durante a produção.
Para carregamento de 5 ul, todos os fragmentos, exceto 250bp, são de 40 ng. O fragmento de 250 pb é de 100 ng.
O marcador é pré-misturado com corante e está pronto para uso.
Carregamento recomendado
2-5 ul
Concentração
Banda em evidência 100 ng / 5 ul
Outras bandas 40 ng / 5 ulCondição de eletroforese recomendada
8 cm, Gel de agarose a 3%, 0,5 × TBE, 5 V/cmConteúdo (bp)
50, 100, 150, 200, 250, 300, 400, 500 -
R$425,92Adicionar ao carrinho
M7012 – DS View Nucleic Acid Stain, 20.000X
Embalagem: 500 ul
Concentração: 20.000xO DSView é uma alternativa ao tradicional corante de brometo de etídio (EB) para detecção de ácido nucléico em géis de agarose. Emite fluorescência verde quando ligado ao DNA ou RNA. O corante DSView tem dois máximos de excitação de fluorescência: em 267 nm e outro em 294 nm. Além disso, também tem uma excitação visível a 491nm.
Armazenamento: guarde a 4ºC por até 2 anos.
Protocolo
1. Preparar 100 ml de solução de gel de agarose (concentração de 0,8 a 2%) e misturar completamente. Coloque o frasco no microondas, aqueça até que a solução esteja completamente limpa e não haja partículas flutuantes pequenas visíveis (cerca de 2 ~ 3 minutos).
2. Adicione 2-5μl de DSViewTM à solução de gel. Agite o frasco suavemente para misturar a solução e evite formar bolhas.
3. Enquanto a solução de gel esfria, despeje-a na bandeja de gel até que os dentes do pente estejam imersos cerca de 1/4 ~ 1/2 na solução de gel.
4. Permitir o gel de agarose esfriar até solidificado. Coloque amostras no gel e corra a eletroforese.
5.Detectar as bandas sob iluminação UV.
-
R$1.677,06O preço original era: R$1.677,06.R$1.080,00O preço atual é: R$1.080,00.Adicionar ao carrinho1kb DNA ladder
M1182 (5x50ug)
Concentração: 104ng/ul
Armazenar a -20°C
Volume estimado: 5x500ul
Descrição
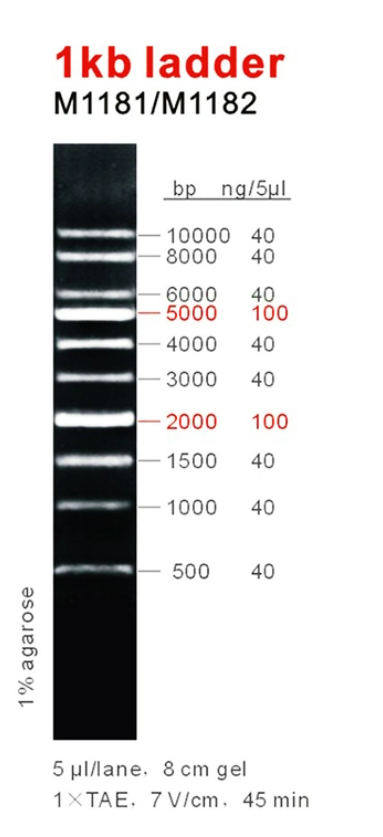
1kb DNA ladder é ideal para determinar o tamanho de fitas duplas de DNA de 500 a 10.000 pares de base. O marcador consiste em 10 fragmentos de dupla fita. Os fragmentos de tamanho 2.000 e 5.000bp estão presentes com maior intensidade para permitir fácil identificação. Todos os fragmentos são precisamente quantificados e misturados durante a fabricação. Para carregamento de 5ul todos os fragmentos têm 40ng, com exceção dos fragmentos 2.000 e 5.000bp que têm 100ng. Este marcador é pré-misturado com tampão de carregamento azul e está pronto para uso.
Carregamento recomendado
2-5 ul por poço
Concentração
Bandas em evidência 100 ng/5ul
Outras bandas 40 ng/5ul
Condições recomendadas para Eletroforese
Gel de agarose 1%, 8cm, 1X TAE, 7 V/cm, 45 min.
Conteúdo (bp)
500, 1.000, 1.500, 2.000, 3.000, 4.000, 5.000, 6.000, 7.000, 8.000 e 10.000