RNase A (Lyophilized Powder), 100mg
R$302,40
RNase A
N9046 (100MG)
Atividade específica: >2.500 u/mg proteínas (>units/mg proteínas)
Formato: contém 100mg de RNase A liofilizada.
Armazenar em temperatura ambiente por até um ano. Para um período maior armazenar em 4°C.
Descrição
RNase A, livre de DNase e proteases é uma endoribonuclase que degraga especificamente fitas únicas de RNA, clivando as ligações de fosfodiéster entre 5’ ribose do nucleotídeo e o grupo fosfato anexado a 3’ ribose de um nucleotídeo de pirimidina adjacente. O 2′, 3′-fosfato cíclico resultante é hidrolisado ao 3′ nucleosídeo fosfato correspondente.
Aplicações
Preparação de DNA genomico e plasmídeos
Remoção do RNA a partir de amostras de proteína recombinante
Ensaios de proteção à ribonuclease
Mapeamento de mutações de uma única base de DNA ou RNA
Controle de Qualidade
A ausência de endodesoxirribonucleases, exodeoxiribonucleases e proteases foi confirmada por testes de qualidade adequados. Funcionalmente testadas para a digestão de RNA em um procedimento de purificação de DNA plasmidial.
Fonte
Pâncreas bovino.
Peso Molecular
13,7 kDa monómero.
Definição de Atividade por Unidade
Uma unidade da enzima provoca um aumento na absorbância de 1,0 a 260nm quando RNA de levedura é hidrolisado a 37°C e pH 5.0
Cinquenta unidades equivalem a aproximadamente equivalente a 1 unidade de Kunitz
Inibição e Inativação
Inibidores: O inibidor mais potente é uma proteína de ~50 kDa a partir de citosol de células de mamíferos, por exemplo, RiboLock™ RNase inibidor.
Outros inibidores: uridina 2′, 3′ vanadato cíclico, 5′-difosfoadenosina 3′-fosfato e 5′-difosfoadenosina 2′-fosfato (2), SDS, dietil pirocarbonato, guanidínio tiocianato 4M mais 0,1 M de 2-mercaptoetanol e íons de metais pesados. Inativado por extração com fenol / clorofórmio.
Inativado por extração com fenol/clorofórmio.
Inativado por aquecimento a 95°C durante 10 minutos.
Disponível por encomenda
| Nota A concentração ótima para RNase A é de 1-100 ug/ml, dependendo da aplicação. |
| A enzima é ativa sob uma grande variedade de condições de reação. Em baixas concentrações de sal (NaCl 0 a 100 mM), a RNase A cliva o RNA de cadeia simples e de cadeia dupla, bem como a cadeia de RNA em híbridos de RNA-DNA. No entanto, em concentrações de NaCl de 0.3M ou superior, a RNase A cliva especificamente o RNA de cadeia simples. |
Produtos relacionados
-
R$327,60
Descrição
A digestão de Hind III de DNA lambda produz 8 fragmentos adequados para uso como
padrões de peso molecular para eletroforese em gel de agarose. DNA / Hind Ⅲ é pré-misturado com tampão de carregamento e está pronto para uso.Condição de eletroforese recomendada
8 cm, gel de agarose 0,7%, 1 × TAE, 7 V / cm, 45 min.Conteúdos (bp)
125, 564, 2.027, 2,322, 4,361, 6,557, 9,416, 23,130.Armazenar
Estável por 3 meses em temperatura ambiente, para armazenamento a longo prazo, armazene a -20 ℃.Atenção!
As extremidades coesivas dos fragmentos 1 e 4 podem causar a formação de banda extra de 27491 bp. Os fragmentos podem ser separados por aquecimento a 65 ° C por 3 minutos antes de carregar a amostra no gel.
-
R$403,20
M7012 – DS View Nucleic Acid Stain, 20.000X
Embalagem: 500 ul
Concentração: 20.000xO DSView é uma alternativa ao tradicional corante de brometo de etídio (EB) para detecção de ácido nucléico em géis de agarose. Emite fluorescência verde quando ligado ao DNA ou RNA. O corante DSView tem dois máximos de excitação de fluorescência: em 267 nm e outro em 294 nm. Além disso, também tem uma excitação visível a 491nm.
Armazenamento: guarde a 4ºC por até 2 anos.
Protocolo
1. Preparar 100 ml de solução de gel de agarose (concentração de 0,8 a 2%) e misturar completamente. Coloque o frasco no microondas, aqueça até que a solução esteja completamente limpa e não haja partículas flutuantes pequenas visíveis (cerca de 2 ~ 3 minutos).
2. Adicione 2-5μl de DSViewTM à solução de gel. Agite o frasco suavemente para misturar a solução e evite formar bolhas.
3. Enquanto a solução de gel esfria, despeje-a na bandeja de gel até que os dentes do pente estejam imersos cerca de 1/4 ~ 1/2 na solução de gel.
4. Permitir o gel de agarose esfriar até solidificado. Coloque amostras no gel e corra a eletroforese.
5.Detectar as bandas sob iluminação UV.
-
R$1.764,00
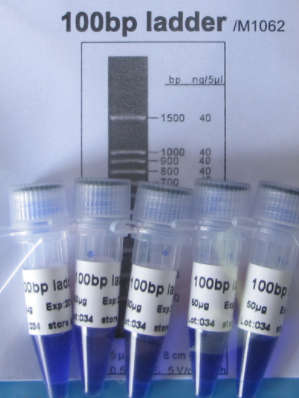
100bp DNA ladderM1062 (5 x 50ug)
Concentração: 100ng/ul
Armazenar a -20°C
Volume estimado: 5x500ul
Descrição
100bp DNA ladder é ideal para determinar o tamanho de DNA de fita dupla de 100 a 1.500 pares de base. O marcador consiste em 11 fragmentos lineares de dupla fita. O fragmento de tamanho 500bp está presente com maior intensidade para permitir fácil identificação. Todos os fragmentos são precisamente quantificados e misturados durante a fabricação. Para aplicação de 5ul, todos os fragmentos têm 40ng, com exceção do fragmento 500bp que tem 100ng. Este marcador é pré-misturado com tampão de aplicação azul e está pronto para uso.
Aplicação recomendada
2-5 ul por poço
Concentração
Banda em evidência 100 ng/5ul
Outras bandas 40 ng/5ul
Condições recomendadas para Eletroforese
Gel de agarose 1.7%, 8 cm, 0.5X TAE, 5 V/cm, 1h.
Conteúdo (bp)
100, 200, 300, 400, 500, 600, 700, 800, 900, 1.000 e 1.500 -
R$1.587,60
1kb DNA ladder
M1182 (5x50ug)
Concentração: 104ng/ul
Armazenar a -20°C
Volume estimado: 5x500ul
Descrição
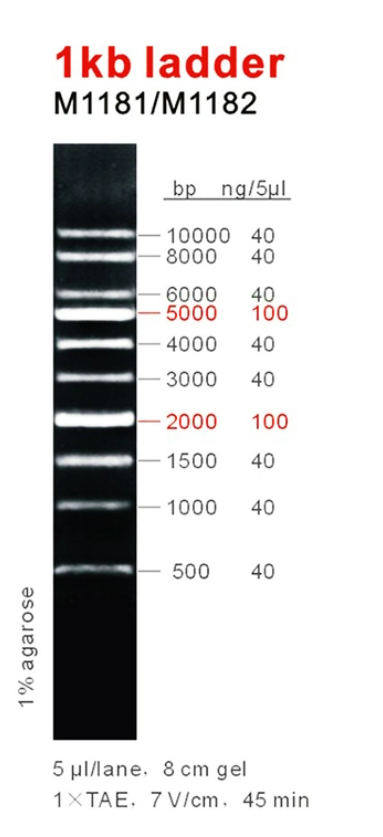
1kb DNA ladder é ideal para determinar o tamanho de fitas duplas de DNA de 500 a 10.000 pares de base. O marcador consiste em 10 fragmentos de dupla fita. Os fragmentos de tamanho 2.000 e 5.000bp estão presentes com maior intensidade para permitir fácil identificação. Todos os fragmentos são precisamente quantificados e misturados durante a fabricação. Para carregamento de 5ul todos os fragmentos têm 40ng, com exceção dos fragmentos 2.000 e 5.000bp que têm 100ng. Este marcador é pré-misturado com tampão de carregamento azul e está pronto para uso.
Carregamento recomendado
2-5 ul por poço
Concentração
Bandas em evidência 100 ng/5ul
Outras bandas 40 ng/5ul
Condições recomendadas para Eletroforese
Gel de agarose 1%, 8cm, 1X TAE, 7 V/cm, 45 min.
Conteúdo (bp)
500, 1.000, 1.500, 2.000, 3.000, 4.000, 5.000, 6.000, 7.000, 8.000 e 10.000