dATP (100mM), 0.5ml
R$236,92
Descrição
dATP (2′-desoxiadenosina 5′-trifosfato) é fornecido como uma solução aquosa 100 mM a pH 7,0.
Aplicações
Para uso em PCR, PCR longo, RT-PCR, síntese de cDNA, extensão de primer, sequenciamento de DNA, marcação de DNA.
Disponível por encomenda
Produtos relacionados
-
R$119,79Adicionar ao carrinho
Conteúdo
Gel Loading Dye, Blue (6X):10 mM Tris-HCL (pH 7.6)
0.03% Bromophenol Blue
60% Glycerol
60 mM EDTADescrição
Gel Loading Dye, Blue (6X) é um tampão de carregamento pré-misturado com um corante de rastreamento para eletroforese em gel de agarose e poliacrilamida não desnaturante.
EDTA é incluído para quelar magnésio (até 10 mM) em reações enzimáticas, parando assim a reação. O azul de bromofenol é o corante de rastreamento padrão para eletroforese.
Declaração de garantia de qualidade
Gel Loading Dye, Blue (6X) é testado para contaminação de endonuclease, exonuclease e atividade RNase.Taxa de migração
O azul de bromofenol migra a aproximadamente 370 bp em um gel de agarose TAE a 1% padrão e 220 bp em um gel de agarose TBE a 1% padrão. -
R$351,45Adicionar ao carrinho
BioMax é uma agarose ideal para procedimentos de rotina de separação de fragmentos de DNA e RNA , assim como produtos de PCR, preparação de plasmídeos e para técnicas de análise, clonagem e blotting.
Características
– Dissolução fácil e gelificação rápida
– Ótima translucidez e baixo background permite uma visibilidade nítida das bandas
– Bandas bem demarcadas e definidas
– Baixissima afinidade para ligação ao DNAAplicações
– BioMax possui uma força de gel alta mesmo em baixas concentrações, taxas de uso é de 0.75 a 2%
– É eficaz in técnicas de blotting e em separação de frações de ácidos nucleicos de 250 bp a 23Kb. -
R$133,10Adicionar ao carrinho
A RNase A, DNase e livre de protease é uma endoribonuclease que degrada especificamente RNA de fita simples nos resíduos C e U. Ele cliva a ligação fosfodiéster entre a 5′-ribose de um nucleotídeo e o grupo fosfato ligado à 3′-ribose de um nucleotídeo de pirimidina adjacente. O fosfato 2′,3′-cíclico resultante é hidrolisado no fosfato 3′-nucleosídeo correspondente.
Aplicações –Preparação de
DNA plasmidial e genômico
–Remoção de RNA de preparações de proteínas recombinantes.
–Ensaios de proteção de ribonuclease
–Mapeamento de mutações de base única em DNA ou RNAFonte
Pâncreas bovino.Peso Molecular
Monômero de 13,7 kDa.Definição de Unidade de Atividade
Uma unidade da enzima causa um aumento na absorbância de 1,0 a 260 nm quando o RNA de levedura é hidrolisado a 37°C e pH 5,0.
Cinquenta unidades são aproximadamente equivalentes a 1 unidade Kunitz. -
R$702,77Adicionar ao carrinho
Descrição
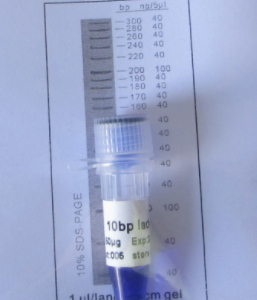
O DNA Ladder de 10 pb é ideal para determinar o tamanho do DNA de fita dupla de 80 a 300 pares de bases. A marcador consiste em 18 fragmentos lineares de fita dupla.
Os fragmentos de 100 pb e 200 pb estão presentes em intensidade aumentada para permitir fácil identificação. Todos os fragmentos são quantificados com precisão e misturados durante a produção. Para carregamento de 5 ul, todos os fragmentos, exceto 100 pb e 200 pb, são de 40 ng.
Os fragmentos de 100 pb e 200 pb são 100 ng. Este marcador é pré-misturado com corante e está pronto para uso.Carregamento recomendado
2-5 ulConcentração
Bandas em evidência 100 ng / 5 ul
Outras bandas 40 ng / 5 ulCondição de eletroforese recomendada
1 ul / por poço, 20 cm, gel de poliacrilamida a 10%, 1 × TBE, 8 V / cm, 3h.Conteúdo (bp)
80, 90, 100, 110, 120, 130, 140, 150, 160, 170, 180, 190, 200, 220, 240, 260, 280, 300.Concentração
168 ng / ul