Takara Bio
Showing 241–260 of 301 results
-
O kit de preparação de amostras de RNA total encalhado SMARTer – HI Mammalian gera bibliotecas para sequenciamento de RNA (RNA-seq), compatível com plataformas Illumina para amostras de mamíferos. O kit foi projetado para trabalhar com faixas de entrada de 100 ng a 1 μg de RNA total. Este kit incorpora a tecnologia RiboGone e SMART e processa a remoção de RNA ribossômico (rRNA) ( sequências de rRNA nuclear 5S, 5.8S, 18S e 28S ), bem como algumas sequências de rRNA mitocondrial ( 12S ), de humanos, camundongos ou ratos RNA total de comprimento total ou cortado, seguido de síntese de cDNA e preparação da biblioteca Illumina. As bibliotecas de RNA-seq preparadas com este kit são indexadas.
-
O kit de preparação de amostras de RNA total encalhado SMARTer – HI Mammalian gera bibliotecas para sequenciamento de RNA (RNA-seq), compatível com plataformas Illumina para amostras de mamíferos. O kit foi projetado para trabalhar com faixas de entrada de 100 ng a 1 μg de RNA total. Este kit incorpora a tecnologia RiboGone e SMART e processa a remoção de RNA ribossômico (rRNA) ( sequências de rRNA nuclear 5S, 5.8S, 18S e 28S ), bem como algumas sequências de rRNA mitocondrial ( 12S ), de humanos, camundongos ou ratos RNA total de comprimento total ou cortado, seguido de síntese de cDNA e preparação da biblioteca Illumina. As bibliotecas de RNA-seq preparadas com este kit são indexadas.
-
O kit de preparação de amostras de RNA total encalhado SMARTer – HI Mammalian gera bibliotecas para sequenciamento de RNA (RNA-seq), compatível com plataformas Illumina para amostras de mamíferos. O kit foi projetado para trabalhar com faixas de entrada de 100 ng a 1 μg de RNA total. Este kit incorpora a tecnologia RiboGone e SMART e processa a remoção de RNA ribossômico (rRNA) ( sequências de rRNA nuclear 5S, 5.8S, 18S e 28S ), bem como algumas sequências de rRNA mitocondrial ( 12S ), de humanos, camundongos ou ratos RNA total de comprimento total ou cortado, seguido de síntese de cDNA e preparação da biblioteca Illumina. As bibliotecas de RNA-seq preparadas com este kit são indexadas.
-
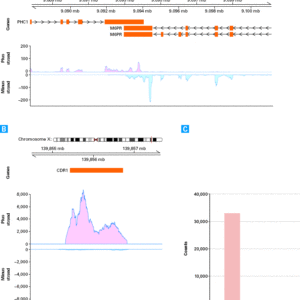
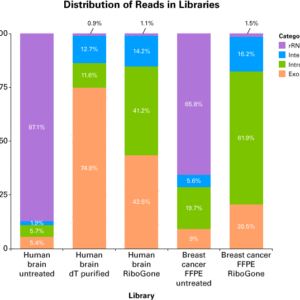
O kit de preparação de amostras de RNA total SMARTer – mamíferos de baixa entrada fornece uma solução completa para análise de RNA total sensível e simplificada. O kit foi projetado para funcionar com uma ampla gama de quantidades de entrada (10–100 ng) de RNA total de qualquer qualidade. Uma variedade de amostras de humanos, ratos e camundongos pode ser usada, incluindo RNA total de material FFPE, amostras de tecidos, etc. O kit fornece análise de transcriptoma completo com medição precisa da orientação da fita, cobertura imparcial, mapeamento de transcrição alta e contagens de genes.
-
R$39.401,25
O kit SMARTer Stranded Total RNA-Seq v3 – Pico Input Mammalian é usado para gerar bibliotecas de RNA-seq específicas de fita para sequenciamento Illumina a partir de entradas de 250 pg–10 ng de RNA total purificado ou de 10–1.000 células intactas. Este kit incorpora a tecnologia proprietária SMART (Switching Mechanism at the 5’ end of RNA Template) da Takara Bio e inclui refinamentos no método SMARTer para RNA-seq de fita que simplificam o fluxo de trabalho de preparação da biblioteca e melhoram o desempenho do sequenciamento. Este método foi desenvolvido para trabalhar com RNA total de alta ou baixa qualidade, não requer métodos ou kits adicionais de remoção de rRNA e produz bibliotecas de sequenciamento que retêm informações da fita de origem. A remoção integrada de cDNAs derivados de rRNA — normalmente presentes em alta abundância após a síntese de cDNA a partir de entradas de RNA total — torna o fluxo de trabalho extremamente sensível, produzindo dados altamente reprodutíveis com baixo mapeamento para rRNA. O novo design de biblioteca apresentado neste kit atualizado adiciona um identificador molecular exclusivo (UMI) de 8 nucleotídeos (nt) por meio da etapa de transcrição reversa para mitigar o potencial viés de PCR, bem como fornecer aos clientes informações adicionais para quantificação de transcrição, especificamente para variantes verdadeiras e mutações raras. Este kit inclui o SMARTer RNA Unique Dual Index Kit – 24U (Takara Bio, Cat. No. 634451). O SMARTer RNA Unique Dual Index Kit – 96U Set A e B (Cat. #s 634452 e 634457) estão disponíveis para compra. Juntos, eles oferecem até 192 índices duais exclusivos para multiplexação.
-
R$3.320,25
O SMARTScribe Reverse Transcriptase é uma enzima de alto desempenho que realiza a síntese imparcial de cDNA, permitindo a amplificação e a construção de bibliotecas a partir de qualquer transcrição de RNA. SMARTScribe RT é uma transcriptase reversa do vírus da leucemia murina de Moloney modificada que gera cDNA longo e completo (até 14,7 kb), preservando as proporções relativas de transcrição da amostra de RNA original. Nosso processo de purificação proprietário e rigorosos padrões de controle de qualidade garantem que praticamente todas as nucleases contaminantes sejam removidas do SMARTScribe RT. Foi especialmente formulado para uso com todos os nossos kits SMART.
-
R$1.539,00
O SMARTScribe Reverse Transcriptase é uma enzima de alto desempenho que realiza a síntese imparcial de cDNA, permitindo a amplificação e a construção de bibliotecas a partir de qualquer transcrição de RNA. SMARTScribe RT é uma transcriptase reversa do vírus da leucemia murina de Moloney modificada que gera cDNA longo e completo (até 14,7 kb), preservando as proporções relativas de transcrição da amostra de RNA original. Nosso processo de purificação proprietário e rigorosos padrões de controle de qualidade garantem que praticamente todas as nucleases contaminantes sejam removidas do SMARTScribe RT. Foi especialmente formulado para uso com todos os nossos kits SMART.
-
R$20.719,50
É uma RNA polimerase dependente de DNA que exibe uma alta especificidade para sequências do promotor SP6 do bacteriófago. A enzima pode incorporar trifosfatos de nucleotídeos marcados ou não marcados em um transcrito de RNA. Grandes quantidades de RNA podem ser sintetizadas a partir de uma sequência de DNA clonada a jusante de um promotor SP6. A SP6 RNA Polimerase é fornecida em 10 mM de fosfato de potássio (pH 7,9), 150 mM de NaCl, 1 mM de DTT, 0,1 mM de EDTA e 50% de glicerol.
-
É uma RNA polimerase dependente de DNA que exibe uma alta especificidade para sequências do promotor SP6 do bacteriófago. A enzima pode incorporar trifosfatos de nucleotídeos marcados ou não marcados em um transcrito de RNA. Grandes quantidades de RNA podem ser sintetizadas a partir de uma sequência de DNA clonada a jusante de um promotor SP6. A SP6 RNA Polimerase é fornecida em 10 mM de fosfato de potássio (pH 7,9), 150 mM de NaCl, 1 mM de DTT, 0,1 mM de EDTA e 50% de glicerol.
-
R$3.633,75
Stellar Competent Cells (dam-/dcm-) são uma cepa de E. coli HST04 que não possui os fatores genéticos (dam e dcm) necessários para a metilação do DNA. Os plasmídeos preparados com este produto podem ser cortados por enzimas de restrição que são normalmente bloqueadas por metilação de dam ou dcm. Uma mutação dupla dam/recA é letal, então a cepa parental é recA+. Portanto, segue-se que a transformação do DNA extracelular com sequências repetidas pode resultar em recombinação por recA. Este produto não é um hospedeiro de clonagem adequado. Para transformação, é altamente recomendável usar este produto para construir plasmídeos como mencionado acima. Um vetor pUC19 é fornecido, bem como o meio SOC.
-
R$3.619,50
Stellar Competent Cells é uma cepa de E. coli HST08 que fornece alta eficiência de transformação. Essas células podem ser usadas em uma ampla variedade de aplicações – desde a preparação de cDNA e bibliotecas genômicas, até a construção de bibliotecas genômicas de comprimento maior, subclonagem e até mesmo clonagem de DNA metilado. As células estelares competentes não possuem o agrupamento de genes para cortar DNA metilado estranho ( mrr-hsdRMS-mcrBC e mcrA ) e, portanto, são úteis para clonar DNA metilado. As células também podem ser usadas para triagem azul/branco (isto é, complementação α) quando transformadas com vetores contendo o gene lacZα . Este pacote inclui 50 tubos de células competentes (100 ul/tubo), meio SOC e um vetor pUC19.
-
O siRNA sintético geralmente tem uma saliência de dois nucleotídeos desoxitimidina (dTT) em suas extremidades 3′. O Synthetic siRNA Quantitation Core Kit adiciona resíduos de polidesoxiadenina (poli dA) às saliências 3′ dTT e, em seguida, realiza uma reação de transcrição reversa com um primer oligo dT especialmente projetado, permitindo a preparação de DNA complementar a partir do siRNA sintético. A quantificação de alta sensibilidade de siRNA sintético pode ser alcançada usando o cDNA preparado como modelo na PCR em tempo real de corante verde intercalado com TB Green Premix Ex Taq II (Tli RNase H plus) ou um produto similar.
O kit principal de quantificação de siRNA sintético foi projetado para quantificar siRNA sintético quando usado em combinação com análise de PCR em tempo real e é usado para testar a quantidade residual do siRNA administrado em amostras de RNA total extraídas de células, tecidos, sangue e outras amostras.
-
T-Vector pMD19 (Simples) é um vetor linearizado com uma única timidina 3′-terminal em ambas as extremidades. As extremidades em T no local de clonagem melhoram a eficiência da ligação de produtos de PCR que contêm saliências A nas extremidades 3′. Os múltiplos locais de clonagem no lac Zsequência gênica foi deletada deste vetor, mas sua atividade de β-galactosidase não é interrompida. Portanto, colônias transformantes contendo plasmídeos recombinantes podem ser identificadas por triagem azul/branco. Devido à falta de múltiplos locais de clonagem no vetor, o produto de PCR inserido não pode ser recortado usando enzimas de restrição. Quando o fragmento de DNA inserido é recortado do vetor, os primers de PCR devem ser usados para adicionar um sítio de restrição à extremidade 5′ para digestão e subclonagem da enzima de restrição. O T-Vector pMD19 (Simples) é fornecido com um DNA de Inserção de Controle (500 pb) para reações de controle positivo.
-
R$1.083,00
A T4 DNA Ligase é uma enzima de ligação que pode ser usada para unir fragmentos de DNA catalisando a formação de ligações fosfodiéster entre os terminais 5′ fosfato e 3′ hidroxila justapostos no DNA de fita dupla usando ATP como coenzima. Tanto a ligação de DNA de extremidade cega quanto a coesiva, bem como o reparo de nick de fita simples de DNA, RNA e DNA/RNA, são possíveis usando a ligase de DNA de T4.
-
A T4 DNA Polimerase catalisa a incorporação de nucleotídeos no DNA de fita dupla na direção 5’→3′. Possui uma forte atividade de exonuclease 3’→5′ (revisão), mas não exibe atividade de exonuclease 5’→3′. A T4 DNA Polimerase é fornecida em 200 mM de fosfato de potássio (pH 6,5), 1 mM de DTT e 50% de glicerol.
-
R$7.495,50
A T4 DNA Polimerase catalisa a incorporação de nucleotídeos no DNA de fita dupla na direção 5’→3′. Possui uma forte atividade de exonuclease 3’→5′ (revisão), mas não exibe atividade de exonuclease 5’→3′. A T4 DNA Polimerase é fornecida em 200 mM de fosfato de potássio (pH 6,5), 1 mM de DTT e 50% de glicerol.
-
A T4 RNA Ligase catalisa a formação de ligações fosfodiéster entre ácidos nucleicos de fita simples com terminais 5′-fosfato e 3′-hidroxil. A enzima requer ATP para a atividade. A taxa de atividade é mais alta para a ligação RNA-RNA, menor para a ligação RNA-DNA e muito baixa para a ligação DNA-DNA. A T4 RNA Ligase é fornecida em Tris-HCl 20 mM (pH 7,5), NaCl 50 mM, DTT 1 mm, EDTA 0,1 mM e glicerol a 50%. Cat. # 2050B contém 5 de Cat. #2050A. Consulte Cat. # 2050A para documentação e recursos completos do produto.
-
A T4 RNA Ligase catalisa a formação de ligações fosfodiéster entre ácidos nucleicos de fita simples com terminais 5′-fosfato e 3′-hidroxil. A enzima requer ATP para a atividade. A taxa de atividade é mais alta para a ligação RNA-RNA, menor para a ligação RNA-DNA e muito baixa para a ligação DNA-DNA. A T4 RNA Ligase é fornecida em Tris-HCl 20 mM (pH 7,5), NaCl 50 mM, DTT 1 mm, EDTA 0,1 mM e glicerol a 50%. Cat. # 2050B contém 5 de Cat. #2050A. Consulte Cat. # 2050A para documentação e recursos completos do produto.
-
Takara CBB Protein Safe Stain é um reagente de coloração de proteínas altamente sensível baseado em Coomassie Brilliant Blue G-250. Este produto pode ser usado para corar rapidamente os géis SDS-PAGE ou PAGE nativos. Permite a visualização de bandas de proteína aproximadamente 5 minutos após o início do processo de coloração e oferece máxima sensibilidade após 60 minutos de coloração. Os géis corados podem ser descorados com água desionizada para remover a coloração de fundo. Takara CBB Protein Safe Stain pode detectar bandas contendo apenas 8 ng de proteína. Pode ser manuseado com segurança, pois não contém metanol ou ácido acético.
-
Este reagente é projetado para permitir a extração em uma etapa de DNA pronto para PCR de tecidos embebidos em parafina fixados em formalina a 10%. O protocolo de extração de uma etapa elimina as etapas laboriosas de desparafinização, extração com solvente orgânico e digestão enzimática exigidas em protocolos padrão. A preparação do reagente DEXPAT de DNA pronto para PCR leva apenas 25 minutos, contra 2 a 3 dias para métodos de extração convencionais.